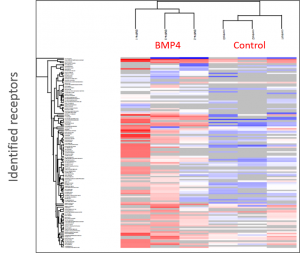
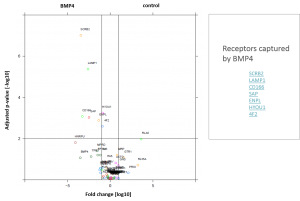
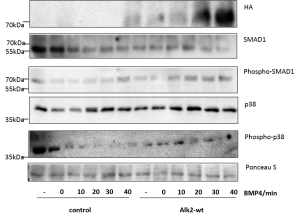
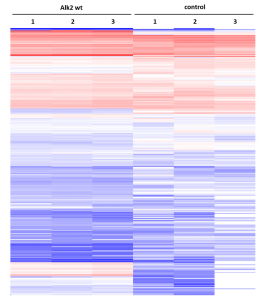
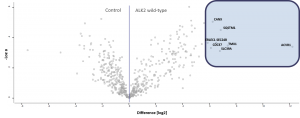
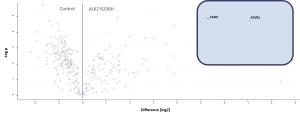
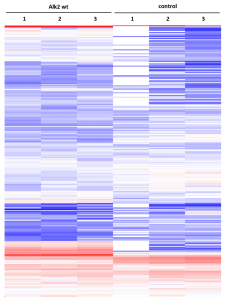
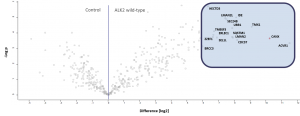
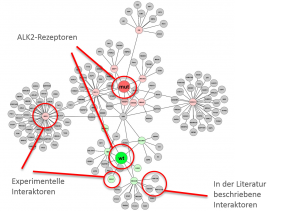
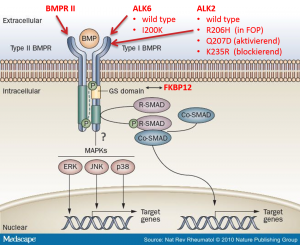
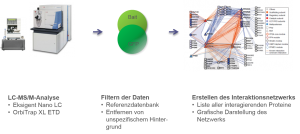
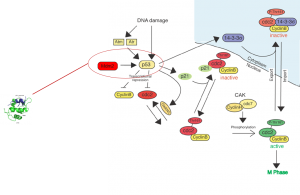
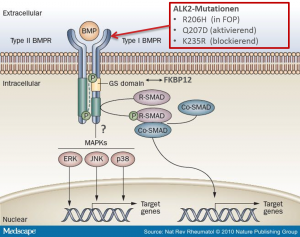
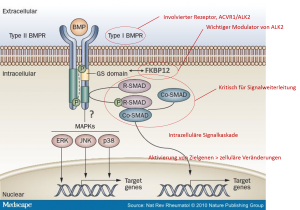
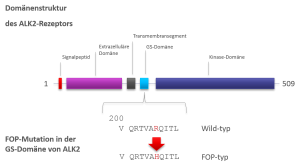
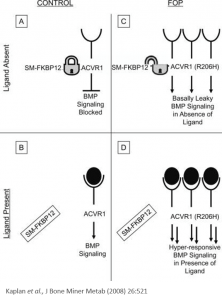
Testen von komplexeren Zellmodellen
In einem nächsten Schritt wurde ein Zellmodell gesucht, welches physiologisch noch näher bei der in vivo-Situation von FOP liegt.
- Zu diesem Zweck wurden 3 verschiedene Zellmodelle getestet:
- HUVEC (Human umbilical vein endothelial cells)
- U2OS (human osteosarcoma cells)
- Jurkat (immortalized T lymphocytes)
Alle 3 Modelle sind relevant für die entzündlichen Reaktionen und Differenzierung zu Knochen, welche in FOP stattfindet.
Die Modelle werden auf folgende Parameter getestet:
- Kultivierbarkeit
- BMP-Signalweg aktiv und stimulierbar mit BMP4
- Transfektionseffizienz (Einbringen der Konstrukte, welche für die Zielproteine kodieren)
Kultivierung von HUVEC, U2OS und Jurkat
Nachfolgend sind die Eigenschaften der drei Zelllinien zusammengefasst:
1. HUVEC (Human umbilical vein endothelial) cells
HUVECs werden aus normaler menschlicher Nabelschnur isoliert. Es handelt sich um Primärzellen, welche nach der Isolation eingefroren werden und nach dem Auftauen durch ca. 16 Passagen expandiert werden können.
HUVECs werden oft für physiologische und pharmakologische Studien verwendet, wie etwa Untersuchungen zum Transport von Makromolekülen, Blutgerinnung oder Fibrinolyse. HUVECs exprimieren Komponenten des BMP-Signalwegs und sind deshalb auch zum Studium von FOP (Fibrodysplasia ossificans progressiva) geeignet.
HUVEC-Zellen in Kultur
2. U2OS (human osteosarcoma) cells
U2OS ist eine humane Osteosarcoma-Linie, welche 1964 aus einem moderat differenziertem Sarkom des Schienbeinknochens etabliert wurden. U2OS exprimieren ebenfalls Komponenten des BMP-Signalweges und können mit BMP4 stimuliert werden
U2OS-Zellen in Kultur
2. Jurkat cells (immortalized human T lymphocytes)
Jurkat sind immortalisierte humane T-Lymphozyten, welche 1970 aus peripherem Blut eines Leukämie-Patienten etabliert wurden.
Jurkat Zellen werden häufig für Virusstudien und im Zusammenhang mit molekularen Mechanismen bei der Entstehung von Krebs eingesetzt und exprimieren eine Reihe von Chemokin-Rezeptoren, ebenso wie BMP-Rezeptoren.
Im Gegensatz zu HUVEC- und U2OS-Zellen sind Jurkat-Zellen nicht adhärent, sondern werden in Suspension kultiviert.
Jurkat-Zellen in Kultur
Voruntersuchungen an HUVEC, U2OS und Jurkat Zellen
Alle drei Zellmodelle werden zunächst auf folgende Parameter getestet:
- Kultivierbarkeit
- BMP-Signalweg aktiv und stimulierbar mit BMP4
- Transfektionseffizienz (Einbringen der Konstrukte, welche für die Zielproteine kodieren)
Dabei zeigten sich relativ rasch zwei Schwierigkeiten:
- HUVECs waren schwer kultivierbar, mit geringen Ausbeuten und langsamen Wachstumsraten
- Jurkat-Zellen waren trotz der Anwendung verschiedener Protokolle nicht mit einer ausreichenden, reproduzierbaren Effizienz transfektierbar
- Da die Transfektion zur Einbringung der Schlüsselproteine eine Grundvoraussetzung darstellt, wurde die Jurkat-Zellen ausgeschlossen
Test der Funktionalität des Signalwegs
Stimulation des BMP-Signalwegs
Im Anschluss wurde an HUVEC und U2OS gestestet, ob der BMP-Signalweg mit BMP4 stimuliert werden konnte
Dazu wurden die Zellen für 30 min. mit BMP4 stimuliert und jeweils bei 0, 10 und 30 min. Proben genommen
Aktivierung des Signalwegs wurde wiederum mittels Western Blotting mit einem anti P-Smad Antikörper nachgewiesen
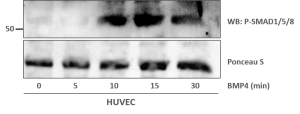
Test der Funktionalität des Signalwegs in HUVEC
- Die HUVECs zeigen eine Antwort auf BMP4-Stimulation
- Daraus kann geschlossen werden, dass der BMP-Signalweg aktiv ist
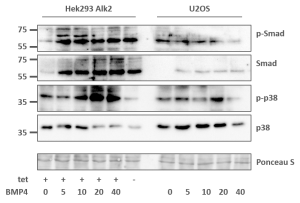
- Die Aktivierung des Signalwegs in U2OS ergibt ebenfalls eine korrekte Stimulation
- Die Stimulation ist weniger stark, als in Alk2-exprimierenden HEK293, was eher der Situation im Menschen entspricht
Resultate
- HUVECs zeigten eine starke Antwort auf BMP4-Stimulation, welche bereits nach ca. 10 min. sichtbar war
- Die Antwort auf BMP4-Stimulation war bei U2OS-Zellen ebenfalls detektierbar, aber deutlich schwächer als in HUVECs
Test der Transfektionseffizienz
- Um eine genügende Expression der Schlüsselproteine zu gewährleisten, muss die Effizienz der Einbringung der DNA-Konstrukte (Transfektionseffizienz) genügend hoch sein
- Die Transfektion der 3 Zelllinien wurde mit verschiedenen Methoden getestet
- Für jede Methode wurden verschiedene Parameter einzeln optimiert
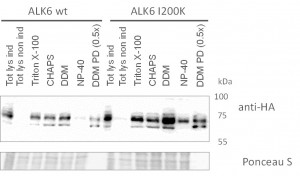
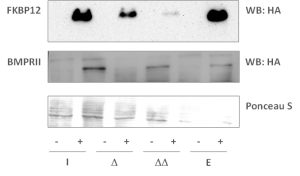
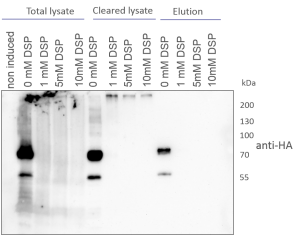
- Die Effizienz der Transfektion wurde mittels Western Blotting mit einem anti HA Antikörper gemessen, welcher direkt das eingebrachte Protein detektiert
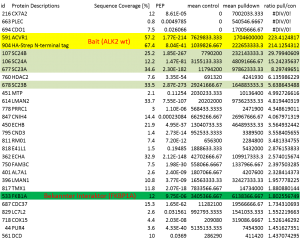
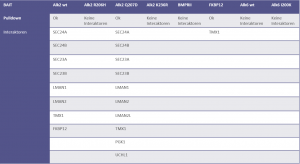
- Effizienz und Reproduzierbarkeit wurden auch mittels Pilot-Pulldowns und Massenspektrometrie-Analyse gemessen
- Im Anschluss wird exemplarisch ein Beispiel für die HUVEC-Zellen gezeigt
HUVEC Transfektionseffizienz
Transfektionen von HUVECs mit dem ALK2-wt Konstrukt mittels Calciumphosphat- und Lipofectamine-Methode. Die Detektion erfolgte mittels eines Antikörpers gegen den HA-tag, welcher C-terminal an ALK2 fusioniert ist.
- Zwei Methoden wurden verwendet:
- Calciumphosphat-Methode (CT)
- Lipofectamine-Methode (LTX)
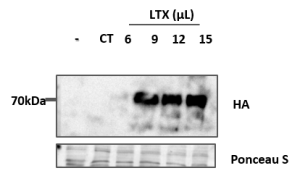
- HUVEC sind transfektierbar mit Lipofectamine
- Die erste Expression des eingebrachten Proteins ist nach ca. 9 Stunden sichtbar
- Die Transfektion mit der Calciumphosphat-Methode zeigt keine detektierbare Expression
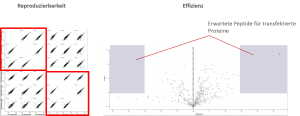
- HUVEC sind transfektierbar
- Die Reproduzierbarkeit der Transfektionen ist innerhalb der Vorgaben
- Die Transfektionseffizienz ist aber ungenügend
Resultate
- Die Transfektion von Jurkat-Zellen zeigte weder eine genügende Transfektionseffizienz, noch eine genügend hohe Reproduzierbarkeit zwischen den einzelnen Transfektionen
- Die Transfektion von HUVEC-Zellen mittels Lipofectamine war reproduzierbar, allerdings war die Transfektionseffizienz ungenügend
- Einzig die U2OS-Zellen zeigten eine genügende Transfektionseffizienz, kombiniert mit einer guten Reproduzierbarkeit
- Aus diesem Grund wurde entschieden, die weiteren Versuche mit U2OS-Zellen durchzuführen